|
|
飞哥推荐:
现在R语言的版本是R4.2.1,这里介绍一下安装最新版的GAPIT如何安装,以及如何运行示例数据,运行处结果。安装前建议,第一电脑用户名需要是英文的,如果是中文的建议新建一个英文的用户名再安装,第二安装最新版的R4.2.1以及Rtoools软件(这个软件单独安装不是R包)。后面我列举了常见的安装错误以及解决方案。
版本情况:
* windows11
*R4.2.1
> sessionInfo()R version 4.2.1 (2022-06-23 ucrt)Platform: x86_64-w64-mingw32/x64 (64-bit)Runningunder:Windows10x64(build22000)
「太长不看版」
在R中运行下面命令即可安装成功PAPIT软件。
#安装GAPIT软件做GWAS分析if(!requireNamespace("BiocManager",quietly=TRUE))install.packages("BiocManager")source("http://zzlab.net/GAPIT/GAPIT.library.R")source("http://zzlab.net/GAPIT/gapit_functions.txt")1. GAPIT官网
张志武老师实验室的网站:
http://www.zzlab.net/GAPIT/
GAPIT说明文档:http://www.zzlab.net/GAPIT/gapit_help_document.pdf
2. GAPIT安装
「错误的做法」
install.packages("GAPIT")「报错:」
>install.packages("GAPIT")Installingpackageinto‘C:/Users/dave/Documents/R/win-library/4.0’(as‘lib’isunspecified)Warningininstall.packages:package‘GAPIT’isnotavailableforthisversionofRAversionofthispackageforyourversionofRmightbeavailableelsewhere,seetheideasathttps://cran.r-project.org/doc/manuals/r-patched/R-admin.html#Installing-packages因为GAPIT不在CRAN上面,所以上面命令是错误的。
「正确的做法」
参考说明文档里的用法,在R中,运行下面命令:
source("http://zzlab.net/GAPIT/GAPIT.library.R")source("http://zzlab.net/GAPIT/gapit_functions.txt")就可以安装了。
「注意,这两条命令会下载安装一些包,默认安装就行。下面将解决一些常见的报错。」
3. 安装报错信息
3.1 Bioconductor 用BioManager
载入需要的程辑包:scatterplot3d错误:WithRversion3.5orgreater,installBioconductorpackagesusingBiocManager;seehttps://bioconductor.org/install此外:Warningmessages:1:Inlibrary(package,lib.loc=lib.loc,character.only=TRUE,logical.return=TRUE,:不存在叫‘LDheatmap’这个名字的程辑包2:Inlibrary(package,lib.loc=lib.loc,character.only=TRUE,logical.return=TRUE,:错误:WithRversion3.5orgreater,installBioconductorpackagesusingBiocManager;seehttps://bioconductor.org/install「解决方法:安装BioManager软件」
if(!requireNamespace("BiocManager",quietly=TRUE))install.packages("BiocManager")然后再运行命令即可成功:
source("http://zzlab.net/GAPIT/GAPIT.library.R")source("http://zzlab.net/GAPIT/gapit_functions.txt")3.2 LDheatmap包找不到
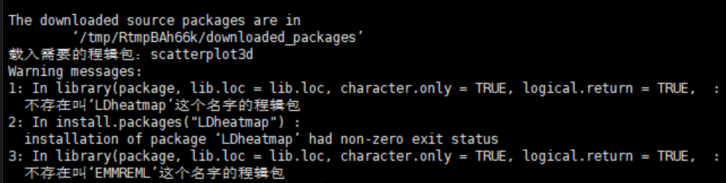
「解决方法:」
install.packages("nloptr")install.packages("LDheatmap")3.3 snpStats包安装错误
「解决方案:」
if(!requireNamespace("BiocManager",quietly=TRUE))install.packages("BiocManager")BiocManager::install("snpStats")「运行成功,没有报错,说明安装成功!」
>source("http://zzlab.net/GAPIT/GAPIT.library.R")载入需要的程辑包:ape载入需要的程辑包:compiler载入需要的程辑包:EMMREML载入需要的程辑包:Matrix载入需要的程辑包:scatterplot3d>source("http://zzlab.net/GAPIT/gapit_functions.txt")4. 测试GAPIT
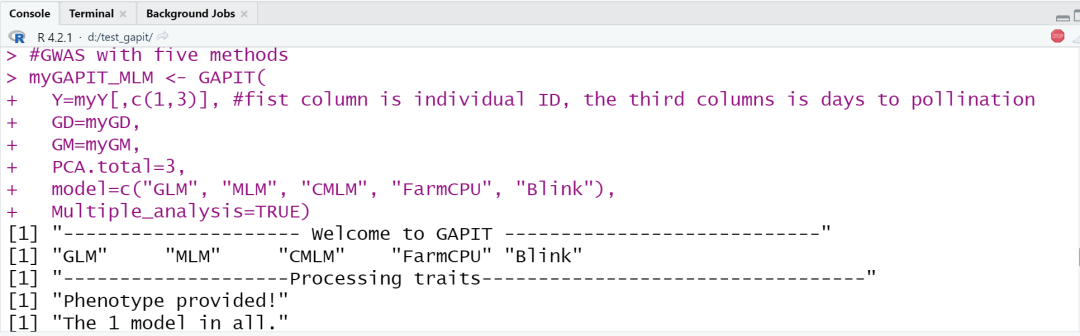
#testGAPIT#ImportdatafromZhiwuZhangLabmyY<-read.table(&#34;http://zzlab.net/GAPIT/data/mdp_traits.txt&#34;,head=TRUE)myGD=read.table(file=&#34;http://zzlab.net/GAPIT/data/mdp_numeric.txt&#34;,head=T)myGM=read.table(file=&#34;http://zzlab.net/GAPIT/data/mdp_SNP_information.txt&#34;,head=T)source(&#34;http://zzlab.net/GAPIT/GAPIT.library.R&#34;)source(&#34;http://zzlab.net/GAPIT/gapit_functions.txt&#34;)#GWASwithfivemethodsmyGAPIT_MLM<-GAPIT(Y=myY[,c(1,3)],#fistcolumnisindividualID,thethirdcolumnsisdaystopollinationGD=myGD,GM=myGM,PCA.total=3,model=c(&#34;GLM&#34;,&#34;MLM&#34;,&#34;CMLM&#34;,&#34;FarmCPU&#34;,&#34;Blink&#34;),Multiple_analysis=TRUE)经过一段时间的运行,结束后,我们可以在工作目录中查看运行的GWAS分析结果。
「运行日志:」
「结果文件:」
结果文件在D盘中的test_gapit文件夹中:
「结果预览:」
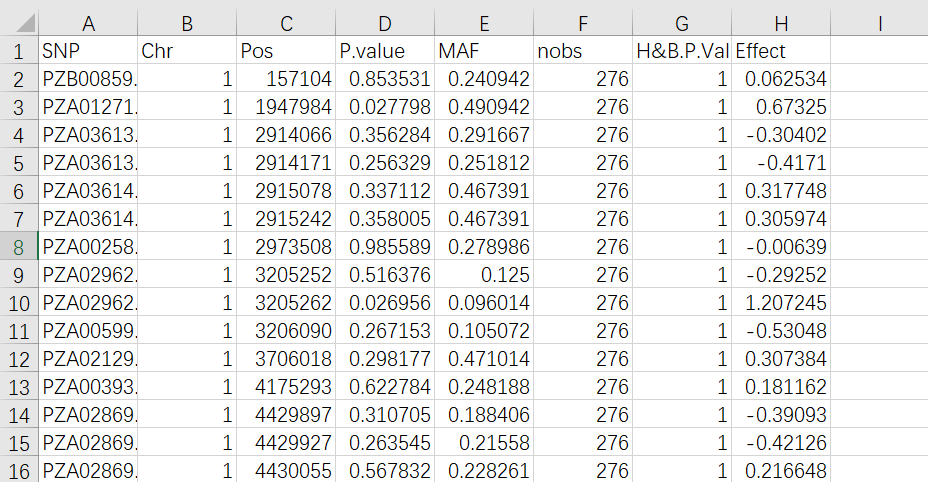
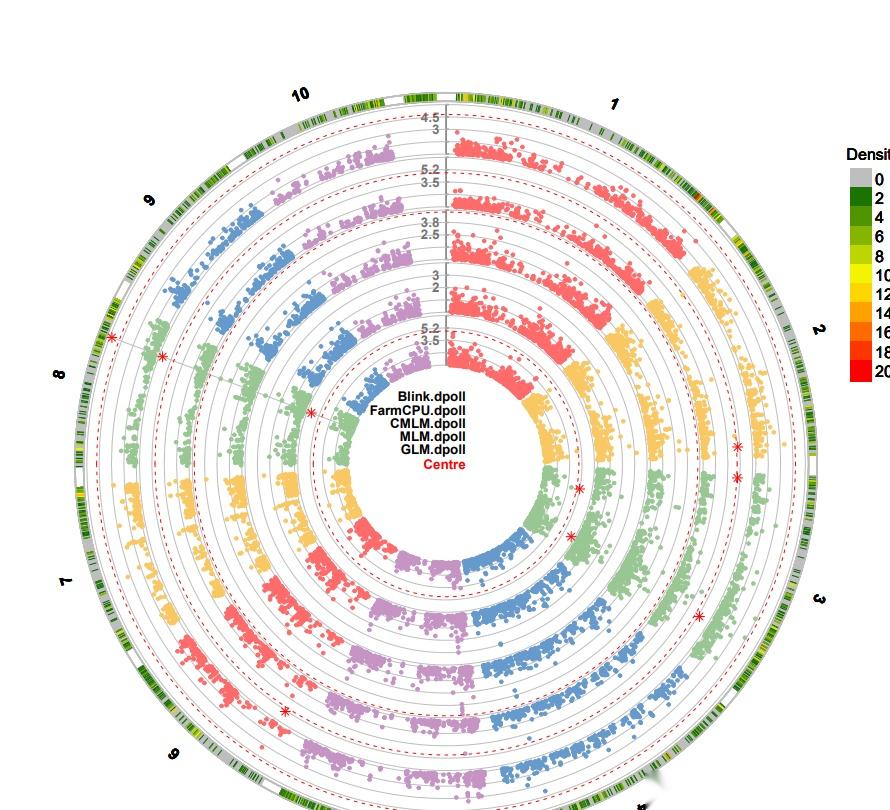
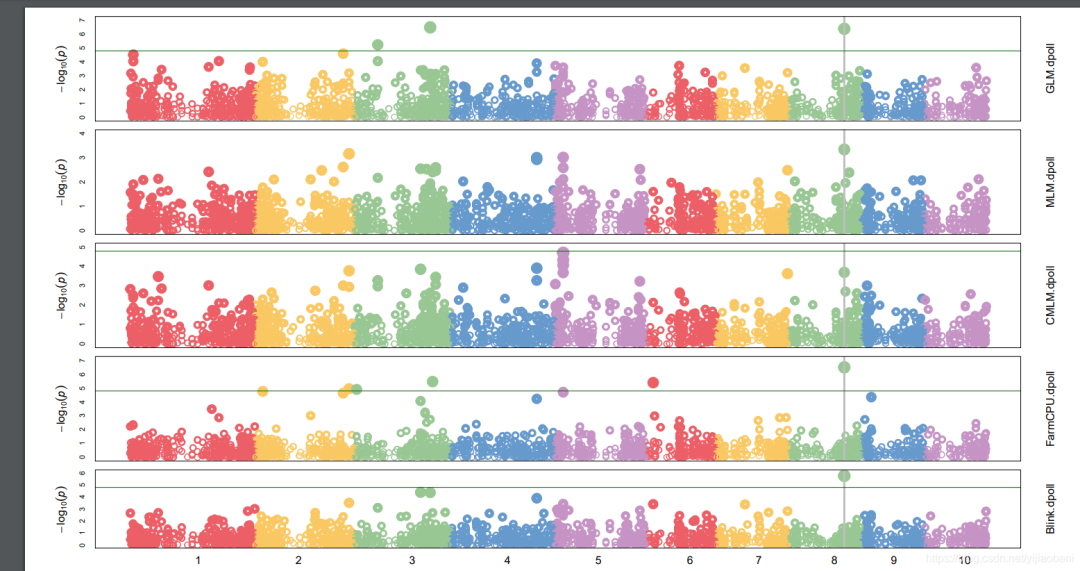
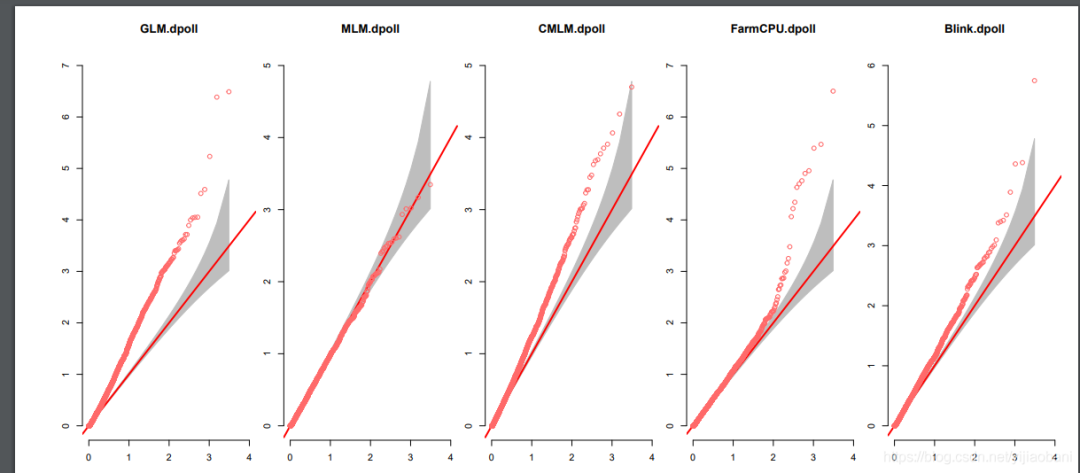
这个软件很强大,很友好,很值得学习使用!
<hr/>分割线
<hr/>
大家好,我是邓飞,一个持续分享的农业数据分析师,这里我将自己公众号的干货内容挑重点罗列一下,方便大家阅读和使用。
1,GWAS学习教程(快来领取 | 飞哥的GWAS分析教程),这个pdf是我将公众号的内容进行了汇总,更方便从头学习GWAS分析,里面配套了数据、代码和讲解,属于干货推荐的Number 1。
2,农学人如何入门数据分析资料汇总(飞哥汇总 | 入门数据分析资源推荐),里面推荐了免费的教程,包括编程、统计和专业书籍。
3,数量遗传学电子书下载(数量遗传学,分享几本书的电子版)
4,R语言电子书线上书籍推荐(学习R语言这几本电子书就够了!)
想要更好的学习和交流,快来加入飞哥的知识星球,这是一个生物统计+数量遗传学+GWAS+GS的社区,在这里你可以向飞哥提问、帮你制定学习计划、跟着飞哥一起做实战项目,冲冲冲。点击这里加入吧:飞哥的学习圈子 |
|